Ces virus qui vivent dans l'intestin humain sont de type bactériophage ; ils sont capables d'infecter les bactéries et les archées. Tous les virus ne sont pas nocifs pour l'Homme. Les bactériophages jouent par exemple un rôle important pour notre santé, en régulant les bactéries qui se trouvent dans notre intestin. « Ils font partie intégrante de l'écosystème intestinal », explique le biochimiste Alexandre Almeida de l'Institut de bio-informatique du Laboratoire européen de biologie moléculaire (EMBL-EBI) et de l'Institut Wellcome Sanger.
Plus de 40 000 génomes viraux de haute qualité
Les virus sont les entités biologiques les plus nombreuses sur Terre avec une population estimée à 1031 particules ! Les bactériophages influencent profondément les communautés microbiennes en fonctionnant comme des vecteurs de transfert horizontal de gènes, en codant des fonctions utiles pour les espèces bactériennes hôtes et en promouvant des interactions co-évolutives dynamiques. Mais pendant longtemps, le phénomène était mal compris des scientifiques.
Ces dernières années, les avancées en matière d'analyse métagénomique ont permis d'obtenir de nouvelles informations fondamentales sur la diversité et les fonctions virales présentes dans le microbiome intestinal humain. Néanmoins, le nombre limité de métagénomes utilisés pour construire les premières bases de données (moins de 700) implique que la majorité de la diversité des phages intestinaux (les virus bactériens) restait non caractérisée et incomplète. La Gut Phage Database (GPD) vient combler ces lacunes : elle comprend plus de 40 000 génomes de phages de haute qualité.
« À notre connaissance, cet ensemble représente la collection la plus complète et la plus précise de génomes de phages intestinaux humains à ce jour », écrivent les auteurs de l'étude. Disposer aujourd'hui d'une base de données complète de génomes de phages de haute qualité ouvre la voie à une multitude d'analyses du virome intestinal humain (la composante virale du microbiote) à une résolution grandement améliorée. Pour Trevor Lawley, microbiologiste au Wellcome Sanger Institute, « la recherche sur les bactériophages connaît actuellement une renaissance ».Pour commencer, ce catalogue a permis d'actualiser les connaissances des scientifiques concernant le comportement viral. Après avoir regroupé l'ensemble du protéome de la GPD en 202'192 grappes de protéines, les chercheurs ont constaté que les fonctions supérieures correspondaient aux protéines de liaison de l'ADN, aux intégrases, aux méthylases, aux peptidases et aux protéines ruban ; cependant, la majorité des protéines phagiques (47,46%) n'ont pas pu se voir attribuer une fonction.
Plus d'un tiers des virus ciblent plusieurs espèces de bactéries
La GPD a également permis d'attribuer un phage spécifique à des espèces hôtes bactériennes. Les chercheurs ont notamment vérifié s'il y avait une préférence pour l'infection phagique via 4 phylums bactériens intestinaux humains communs (Firmicutes, Bacteroidetes, Proteobacteria et Actinobacteriota) : ils ont ainsi détecté une prévalence significativement plus faible des phages dans Actinobacteriota, avec 59% d'isolats infectés contre au moins 70% pour les autres phylums.
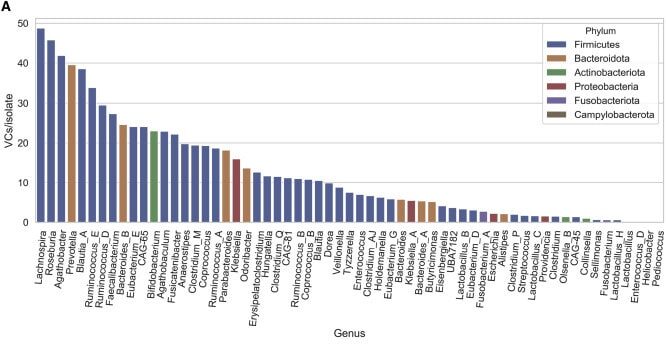
Les chercheurs ont découvert par ailleurs que plus d'un tiers (36%) des grappes virales ne sont pas limitées à infecter une seule espèce, ce qui crée des réseaux de flux de gènes à travers des espèces bactériennes phylogénétiquement distinctes. De plus, ils ont identifié 280 grappes virales réparties dans le monde, y compris un clade nouvellement identifié, très répandu, appelé Gubaphage ; il semble être le deuxième clade de virus le plus répandu dans l'intestin humain, après le groupe que l'on nomme p-crAssphage.
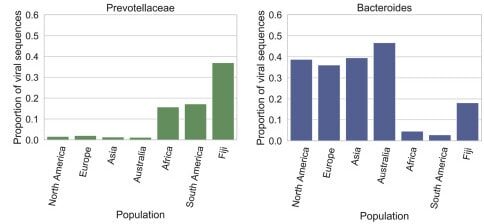
Ce n'est là qu'un aperçu des informations fournies par la GPD nouvellement établie et les chercheurs se réjouissent des découvertes à venir, grâce à cette nouvelle base de connaissances. « Ce catalogue de grande qualité et à grande échelle de génomes de phages améliorera les futures études sur les viromes et permettra une analyse écologique et évolutive des bactériophages intestinaux humains », concluent-ils.



Heu... Il y a comme une erreur dans l'identification.Un virus est une nano-poussière métallique chargée (rayonnement bêta ?) et radioactive. Il n'est donc PAS VIVANT (et reconnu comme tel par le corps scientifique).Alors que les bactéries sont reconnues comme bonne et, quand elles se modifient sont appelées microbes. Donc VIVANTS. Évitons l'amalgame svp.
Maintenant, que (...) Des chercheurs viennent de recenser plus de 140 000 espèces de virus dans nos intestins (...) cela est tout-à-fait possible because que l'on respire 200 000 microbes ou virus par minute et 2 millions en activité physique.Mais... Rien ne nous dit que ces 140 000 espèces de virus soient différentes ! because encore que pour parler du 'corona' (grippes, rhumes en font partie) il n'a pas encore été isolé !! D'où l'IMPOSSIBILITÉ de produire un quelconque vaccin pour le contrer !
Mais revenons aux 200 000 microbes ou virus respirés par minute. A savoir que les nano-particules métalliques expulsées du magma et remontées à la surface par les émissions de gaz de ce dernier (et qui 's'envolent' aux vents pour faire le tour de la Terre) existent depuis 10 000 ans et qu'elles n'ont qu'une durée d'émission que de 3 semaines. Donc, il y a dans notre atmosphère (depuis 10 000 ans) des milliards de km de milliards de ces nano-particules (appelées virus) qui sont INACTIVÉES depuis belle lurette.
Mais, dans le 'ce qui fait peur' il y a que PERSONNE ne sait combien de virus respirés sont actifs !! because qu'il n'existe pas de nano-compteur Geiger capable de trier les qui sont actifs et les qui sont inactifs !